http://genomics.jefferson.edu/proggene/

PROGgeneV2可以分析乳腺、结直肠、卵巢、皮肤、眼、胸腺、肾上腺、胰腺、胃、甲状腺、膀胱、前列腺、尿道、骨、肝、宫颈、神经内分泌系统、肺、脑、肾等器官系统各恶性肿瘤的预后,覆盖度非常广泛
分析类型可选择复发、转移、死亡、脑转移、肺转移等
可选择基因表达量的中位、25%、75%和平均值为界定义高表达和低表达
该网站还可以整合多个基因,即gene expression signature,即联合多基因的表达来分析预后,功能十分强大!但有个缺点,只有mRNA,无lncRNA,microRNA的数据。
https://lncar.renlab.org/
一款专门做lncRNA差异表达、kegg、共表达网络和生存分析的数据库,由中山大学任间教授开发,目前共收录了10种肿瘤的数据 ,膀胱癌、乳腺癌、宫颈癌、结直肠癌、食管癌、胃癌、肝癌、肺癌、卵巢癌、前列腺癌的lncRNA数据。
http://gepia.cancer-pku.cn/index.html
一款TCGA数据库的可视化在线网站,TCGA中包含的癌种GEPIA几乎都有,可分析mRNA、lncRNA、miRNA的数据,覆盖面广,大大方便了我们对TCGA数据库的挖掘
生存分析可选择总生存期和无病生存期,还可自由选择cutoff值(即定义高表达和低表达),不同cutoff值得到的结果可能不同。
http://ualcan.path.uab.edu/analysis.html
UALCAN数据库的生存分析也是基于TCGA数据库,数据包括mRNA和部分lncRNA
点击survival,
http://kmplot.com/analysis/index.php?p=background
因为有个auto select best cufoff选项(对cutoff值进行最优化以判定高表达低表达与预后的关系),该在线网站常能得到p<0.05的阳性结果,为生信分析文章中最常用的数据库之一。
survival 选项中可选择:
OS 总生存期
RFS(recurrence-free survival) 无复发生存期
PPS(post progression survival,进展后的生存期)
DMFS(distant metastasis free survival) 无远处转移生存期
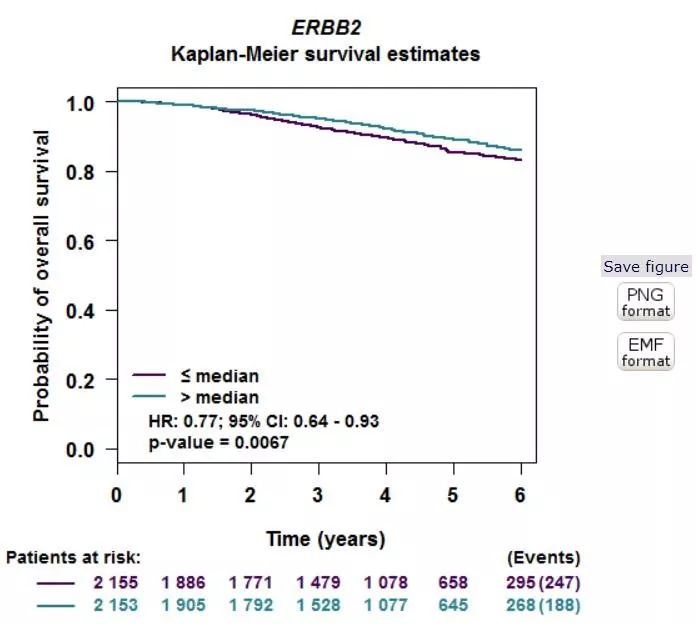
例如我们选择ERBB2后选择auto select best cufoff选项,得到的p=0.013,与前面的GEPIA和UALCAN得到的结果有所不同。
http://www.cbioportal.org/
一款TCGA数据可视化的网站,并包含一部分细胞系和芯片数据,进入官网后再左侧勾选部位,在右侧选择数据集,点击query by gene,
此页面可按需求选择病人亚组,这里我们选择all samples, 输入ERBB2,生存分析结果如下
http://www.oncolnc.org/
一款TCGAmiRNA/mRNA/lncRNA 生存数据分析的网站,优点是cutoff值可以自己随意设置。在首页直接输入感兴的分子
选择感兴趣的癌种,此处选择BRCA,点击Yes please
输入百分之多少定为低表达,百分之多少定为高表达,即设定cutoff值,例如输入50, 50
http://www.oncomir.org/
一款专注于miRNA生存分析的在线工具,在左侧选择custome signatures
选择癌种,输入miRNA的全称,输入cutoff值,点击retrieve survival curve, 结果如下
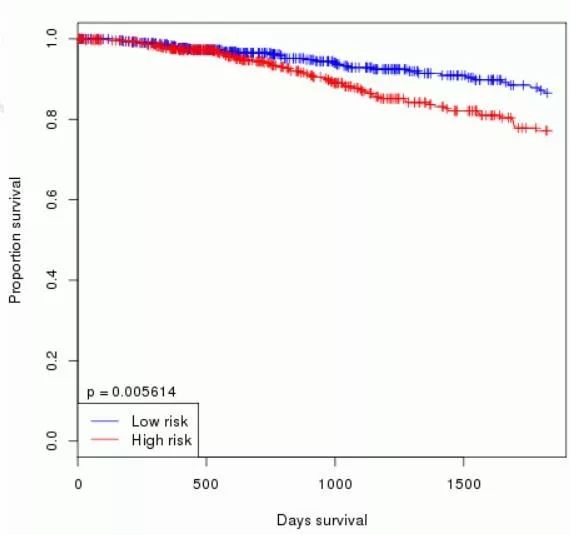
http://bcgenex.centregauducheau.fr/BC-GEM/GEM-Accueil.php?js=1
专注于分析乳腺癌数据,在首页的analysis 菜单下选择prognostic-targeted
选择相应的数据来源和患者亚组后,点击submit
https://biit.cs.ut.ee/methsurv/
基于TCGA 甲基化数据开发的甲基化与肿瘤预后关系的在线分析网站,分析单个CpG位点与患者预后的关系

